[ad_1]
(Noticias de Nanowerk) Un informe histórico de la Universidad de Kansas que aparece en el procedimientos de la Academia Nacional de Ciencias («Simulación de larga escala de tiempo basada en acoplamiento de sistemas de proteínas de tamaño celular a resolución atómica») propone una nueva técnica para modelar la vida molecular con computadoras.
Según el autor principal Ilya Vakser, Director del Programa de Biología Computacional y Centro de Biología Computacional y Profesor de Biociencias Moleculares en KU, investigar el modelado computacional de los procesos de la vida es un paso importante hacia la creación de una simulación funcional de una célula viva con resolución atómica. El avance promete nuevos conocimientos sobre la biología básica de una célula y un tratamiento más rápido y preciso de las enfermedades humanas.
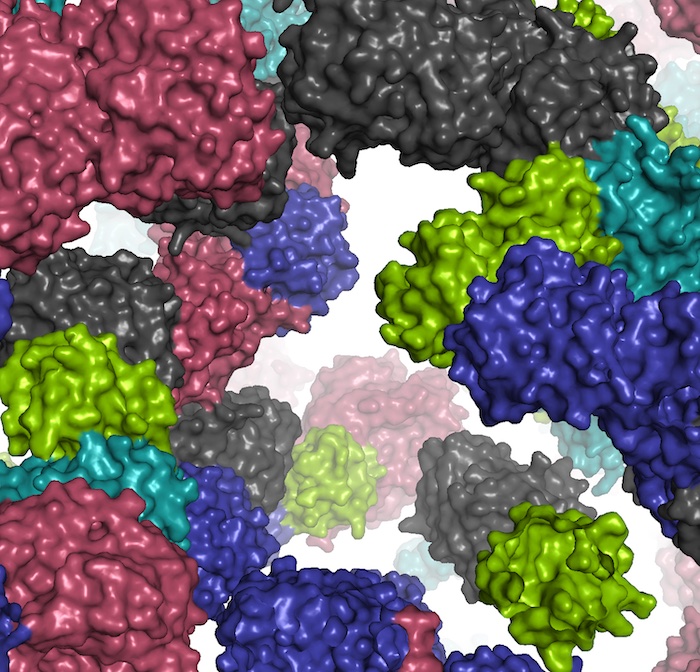
«Es unas 10 o 100.000 veces más rápido que las técnicas de resolución atómica existentes», dijo Vakser. «Esto ofrece oportunidades sin precedentes para caracterizar los mecanismos fisiológicos que ahora están mucho más allá del alcance de los modelos informáticos, obtener información sobre los mecanismos celulares y utilizar este conocimiento para mejorar nuestra capacidad para tratar enfermedades».
Hasta ahora, un obstáculo importante en el modelado de células en una computadora ha sido cómo abordar las proteínas y sus interacciones, que están en el corazón de los procesos celulares. Hasta la fecha, las técnicas establecidas para modelar las interacciones de proteínas se basan en el «acoplamiento de proteínas» o la «simulación molecular».
Según los investigadores, ambos enfoques tienen ventajas y desventajas. Los algoritmos de acoplamiento de proteínas, si bien son excelentes para detectar coordenadas espaciales, no tienen en cuenta la «coordenada de tiempo» o la dinámica de las interacciones de proteínas. Por el contrario, las simulaciones moleculares modelan bien la dinámica, pero estas simulaciones son demasiado lentas o de resolución demasiado baja.
«Nuestro estudio de prueba de concepto combina los dos métodos de modelado y desarrolla un enfoque que puede lograr escalas de tiempo de simulación sin precedentes con una resolución de todos los átomos», escriben los autores.
Los colaboradores de Vakser en el artículo fueron Sergei Grudinin de la Universidad de Grenoble Alpes en Francia; Eric Deeds de la Universidad de California-Los Ángeles; Nathan Jenkins, estudiante de doctorado de KU, y Petras Kundrotas, profesor asistente de investigación en el Programa de Biología Computacional de KU.
Después de conceptualizar la mejor manera de combinar las ventajas de los dos enfoques de modelado de proteínas, el equipo diseñó y codificó un algoritmo para potenciar la nueva simulación.
«El desafío más difícil fue desarrollar el algoritmo que refleja adecuadamente la idea básica simple del enfoque», dijo Vakser.
Pero una vez que lograron este avance, pudieron comenzar a validar el nuevo proceso.
«El paradigma era simple: un golpe de claridad», dijo Vakser. “Los enfoques de simulación existentes pasan la mayor parte del tiempo de cómputo viajando en regiones del sistema de baja probabilidad o alta energía. Todos sabemos dónde están estas áreas. En cambio, la idea era muestrear o viajar solo en las regiones de alta probabilidad y baja energía y omitir las regiones de baja probabilidad estimando las tasas de transición entre los estados de alta probabilidad. El paradigma es tan antiguo como el propio modelado biomolecular y ha tenido un uso generalizado desde que comenzó la era del modelado hace décadas”.
Pero Vakser dijo que hasta la nueva publicación de su equipo, el enfoque no se había aplicado a la cinética de las interacciones de proteínas en el entorno celular, el foco de su estudio.
«Debido a que hay muchos menos estados de alta probabilidad que estados de baja probabilidad, esto nos ha dado una enorme ganancia en la velocidad computacional, de decenas a cientos de miles de veces», dijo Vakser. “Esto se hizo sin pérdida aparente de precisión. Se puede argumentar que se ha ganado precisión porque el protocolo de simulación se basa en las técnicas de «acoplamiento» diseñadas específicamente para la caracterización del ensamblaje de proteínas».
El investigador de KU dijo que su método de simulación celular podría usarse para estudiar la salud humana y tratar enfermedades con un nuevo nivel de precisión.
«El enfoque se puede utilizar para estudiar las vías moleculares que subyacen a los mecanismos de la enfermedad», dijo Vakser. «Se puede utilizar para determinar los efectos nocivos de las mutaciones genéticas a través de patrones alterados de asociación de proteínas: las mutaciones genéticas provocan cambios en la estructura de las proteínas, que a su vez afectan la asociación de proteínas». O podría usarse para identificar objetivos de diseño de fármacos mediante el reconocimiento de elementos críticos en los patrones de asociación de proteínas”.
Según Vakser, la nueva técnica de simulación ofrece muchas oportunidades de investigación prometedoras para el futuro.
«Esto incluye adaptar el enfoque a las interacciones de proteínas con ácidos nucleicos, ARN y ADN», dijo. «También queremos tener en cuenta la flexibilidad de las formas moleculares, correlacionarlas con el cuerpo de estudios experimentales del entorno celular en rápida evolución y aplicar la técnica a un modelo de una célula real, con sus componentes moleculares reales empaquetados juntos».
[ad_2]

